近日,真邁生物用戶俄羅斯莫斯科國立醫(yī)科大學(xué)����、內(nèi)分泌學(xué)研究中心等機構(gòu)在cancers上發(fā)表了題為“A New Approach of Detecting?ALK?Fusion Oncogenes by RNA?Sequencing Exon Coverage Analysis”的科研成果�,基于真邁生物的FASTASeq 300測序平臺�,開發(fā)一種新的生物信息學(xué)方法,利用RNA測序數(shù)據(jù)中的外顯子覆蓋度分析來準(zhǔn)確地預(yù)測臨床上顯著的ALK原癌基因融合�����。在一小部分ALK陽性腫瘤中實現(xiàn)了96%的準(zhǔn)確率(100%的靈敏度�����,94.9%的特異性)�����。
ALK(間變性淋巴瘤激酶)基因重排在多種腫瘤類型中是驅(qū)動突變的常見來源���。常用的檢測ALK融合的方法包括免疫組化(IHC)���、熒光原位雜交(FISH)��、反轉(zhuǎn)錄定量聚合酶鏈反應(yīng)(RT-qPCR)和panel測序����。此外�����,全轉(zhuǎn)錄組測序能夠分析廣泛的癌癥生物標(biāo)志物����,包括失調(diào)基因,分子途徑及腫瘤驅(qū)動基因的基因融合轉(zhuǎn)錄本�。然而,由于在融合斷點處覆蓋不足��,難以發(fā)現(xiàn)融合位點�。基于此���,本文開發(fā)了一種新的生物信息學(xué)方法,可以從RNA測序數(shù)據(jù)中準(zhǔn)確地預(yù)測ALK融合。
丨ALK覆蓋不對稱篩選
文章通過使用TruSight和OncoFu兩個panel對樣本進行RNA建庫���,并使用FASTASeq 300對文庫進行PE75測序���,結(jié)果觀察到在ALK融合陽性樣本中,ALK的覆蓋表現(xiàn)出明顯的不對稱性�。這種不對稱性在樣本的外顯子20-24中尤為突出,意味著這些區(qū)域的表達(dá)水平顯著高于其他外顯子�����。具體來說��,在樣本?ALK_9?中��,文章觀察到明顯的覆蓋不對稱���,與融合陽性狀態(tài)相匹配����。以上表明每個樣本的融合狀態(tài)都可以通過其外顯子覆蓋的差異來推測�����。
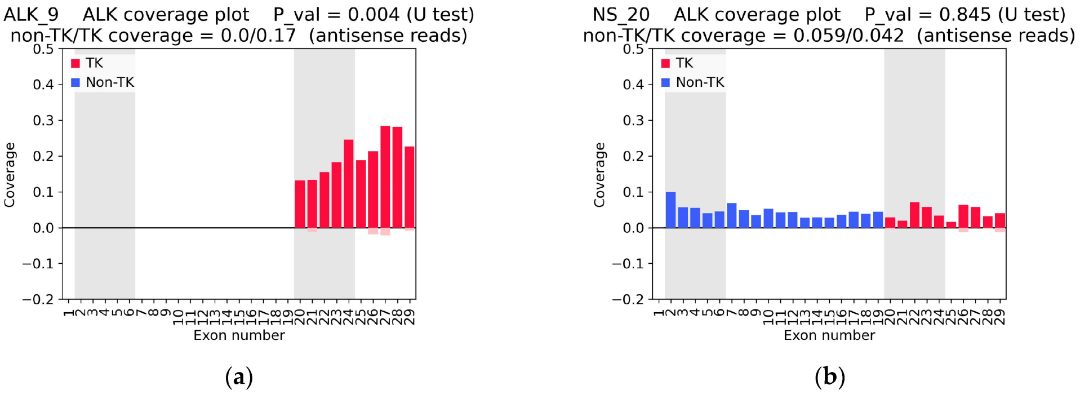
圖1?RNAseq數(shù)據(jù)的ALK覆蓋圖
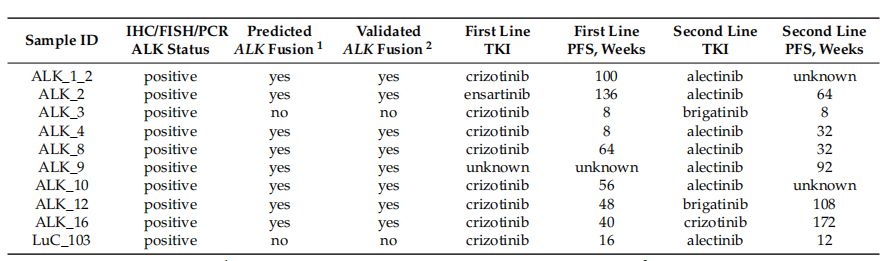
此外,從表1中可以看到���,接受ALK靶向治療的患者中�,預(yù)測為ALK融合陽性的組無進展生存期顯著延長��,進一步支持了文章方法的臨床相關(guān)性�。表1 ALK靶向治療患者信息表
丨TruSight數(shù)據(jù)驗證ALK覆蓋不對稱
圖2展示了基于TruSight數(shù)據(jù)的ALK基因覆蓋圖,主要目的是分析不同樣本的ALK覆蓋不對稱性�����。數(shù)據(jù)顯示��,確認(rèn)有ALK融合的樣本在其ALK基因的覆蓋測量上表現(xiàn)出明顯的不對稱性(ALK_10)��,而在未確認(rèn)融合的樣本中(NS_20)���,這種不對稱性則不明顯��。圖中的結(jié)果強調(diào)了ALK覆蓋不對稱性在腫瘤樣本中預(yù)測ALK融合的重要性�,尤其是在基因的酪氨酸激酶(TK)區(qū)段的覆蓋情況����。
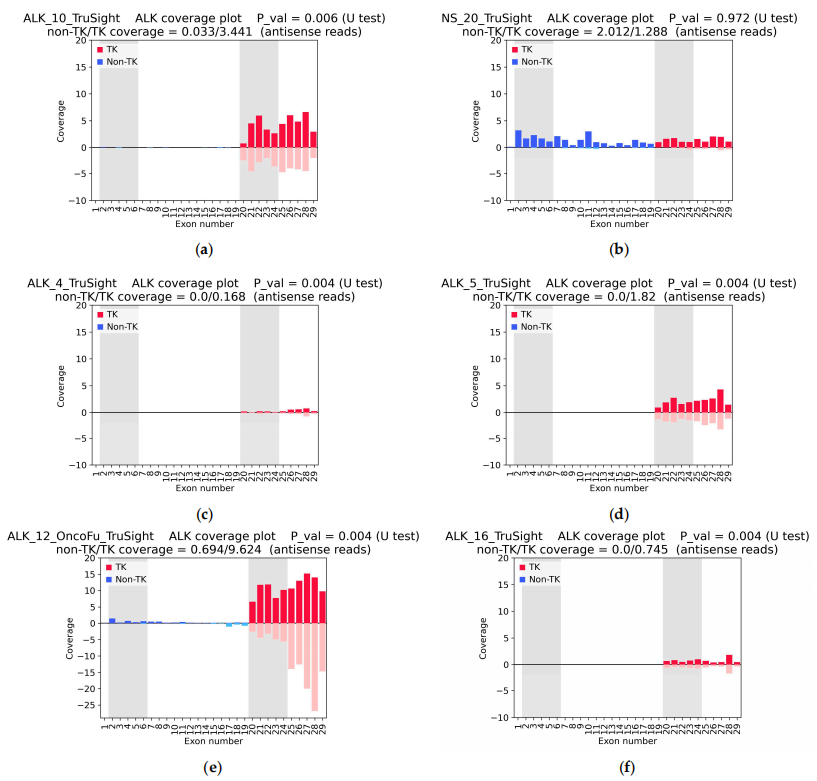
圖2?基于TruSight數(shù)據(jù)的ALK基因覆蓋結(jié)果圖
這項研究表明通過RNA測序外顯子覆蓋率分析���,能夠有效檢測ALK基因融合�。研究顯示,該新穎的生物信息學(xué)方法改善了傳統(tǒng)基因融合檢測技術(shù)的準(zhǔn)確性�����,能夠達(dá)到96%的驗證準(zhǔn)確率�����,其中敏感性為100%���,特異性為94.9%��。
Zakharova G, Suntsova M, Rabushko E, Mohammad T, Drobyshev A, Seryakov A, Poddubskaya E, Moisseev A, Smirnova A, Sorokin M, Tkachev V, Simonov A, Guguchkin E, Karpulevich E, Buzdin A. A New Approach of Detecting ALK Fusion Oncogenes by RNA Sequencing Exon Coverage Analysis. Cancers (Basel). 2024 Nov 16;16(22):3851. doi: 10.3390/cancers16223851. PMID: 39594806.